推荐产品
公司新闻/正文
「青莲客户文献」宏蛋白组组学技术用于脲酶蛋白多样性研究
人阅读 发布时间:2021-11-26 10:31
「青莲客户文献」宏蛋白组组学技术用于脲酶蛋白多样性研究
2020年9月18号, 来自华中农业大学和中国农业科学院动物研究所动物营养国家重点实验室的团队在Frontiers in Microbiology期刊上在线发表了题为“Pipeline for Targeted Meta-Proteomic Analyses to Assess the Diversity of Cattle Rumen Microbial Urease”的研究论文,该研究开发了一种有针对性的宏蛋白质组学研究方法来分析瘤胃脲酶蛋白的多样性。包括前处理中对蛋白质提取(液氮冷冻研磨时间)、蛋白质消化状态(溶液中或凝胶中)以及所用消化酶(胰蛋白酶或Glu-C/Lys-C)进行了优化,并通过LC-MS/MS对酶解后的多肽进行分析(青莲百奥提供技术支持)。该方法为在其他生态系统中进行有针对性的宏蛋白质组学分析提供了指南。

取样策略
使用瘤胃插管从3头牛身上收集瘤胃食糜样品,并通过四层纱布过滤以分离瘤胃液。
研究思路

实验结果
冷冻研磨对蛋白质浓度和脲酶活性的影响
为了评估冷冻研磨方法在蛋白质提取中的适用性,评估了冷冻研磨持续时间对脲酶活性和蛋白质浓度的影响。 结果表明,与冷冻研磨3或5分钟相比,在液氮中冷冻研磨4分钟可使脲酶活性(955.73 nmol/min/mg)和蛋白质浓度(137.73µg/mL)最大化(图1)。

图1. 冷冻研磨对蛋白质浓度和脲酶活性的影响
不同消化方法对瘤胃微生物脲酶宏蛋白质组学分析的影响
评估了四种不同的消化方法(胰蛋白酶溶液酶切、胰蛋白酶胶内酶切、Glu-C/LysC溶液酶切和Glu-C/Lys-C胶内酶切),以选择瘤胃微生物脲酶宏蛋白质组学分析的最佳方法。采用Peaks软件对不同方法的数据进行检索,图2A显示了四种不同消化方法的实际鉴定结果。胰蛋白酶胶内酶切优于其他消化方法,在肽段谱图匹配数(PSM)、匹配到数据库的肽段数和非数据库肽段数、蛋白鉴定数量均最多。该方法比其他方法至少多了37.72%的肽段(来自数据库)和103.07%的蛋白检出率。此外,胰酶胶内酶切也检测到最多的独有肽段(来自数据库)和蛋白质,分别为38%和42%(图2B,C)。对于MS/MS扫描(二级谱图数),无论是溶液酶切还是胶内酶切,Glu-C/Lys-C消化表现出比胰蛋白酶消化略好的性能。

图2. 瘤胃微生物脲酶宏蛋白质组学分析中不同消化方法的比较
瘤胃微生物脲酶多样性
采用胰酶胶内酶切的方法,在多肽和蛋白质水平上研究瘤胃微生物脲酶的多样性。共从数据库中鉴定到2720个肽段,132个蛋白;非数据库的肽共鉴定出4008个。鉴定到的蛋白质分别来自海洋原绿球菌(Prochlorococcus marinus)、海尔曼螺杆菌(Helicobacter heilmannii)、Thalassobacillus devorans、芽孢乳杆菌(Sporolactobacillus sp. THM7-4)、纤维化纤维菌(Cellulosimicrobium cellulans)、嗜冷芽孢八叠球菌(Sporosarcina psychrophila)和一些未知菌。这些数据表明瘤胃微生物脲酶的蛋白质多样性。此外,在多肽水平上,59.57%的多肽是非数据库来源的(图3A),表明瘤胃中存在许多未知的微生物脲酶。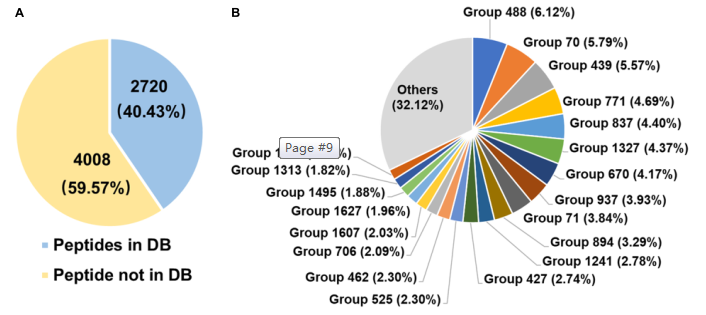
图3. 瘤胃微生物脲酶多样性
小结
为了分析瘤胃微生物脲酶的多样性,该研究开发了一种结合高脲酶活性的蛋白提取和胰蛋白酶消化凝胶内蛋白的有针对性的宏蛋白组学分析方法。脲酶蛋白具有较高的多样性,这些蛋白主要来自原绿球菌(Prochlorococcus)、螺杆菌(Helicobacter)和一些不可培养的细菌。该方法不仅扩展了对牛瘤胃中高活性脲酶的理解,也为在其他复杂生态系统中进行有针对性的宏蛋白质组分析提供了指导。
用于评估牛瘤胃微生物脲酶多样性的宏蛋白质组学分析方法
期刊名称:Frontiers in Microbiology
影响因子:4.235
样本选择:牛瘤胃液样本
技术策略:LC-MS/MS
搜库软件:Peaks(可实现非数据库来源的肽段检索)
更多技术服务敬请来电咨询
010-53395839