推荐产品
公司新闻/正文
「青莲聚焦」蛋白相互作用研究神器——STRING
人阅读 发布时间:2021-12-22 09:59

蛋白质及其功能相互作用构成了细胞机制的骨架。为了充分理解生物现象,需要考虑它们的互作网络,但关于蛋白-蛋白关联的现有信息是不完整的,并且显示出不同程度的注释分散度和可靠性。STRING 数据库旨在收集、评估和整合所有可公开获得的蛋白-蛋白相互作用信息资源,并通过计算机预测来补充这些信息。其目标是实现一个全面的和客观的全球网络,包含直接的(物理)和间接的(功能)互作信息。
数据库内容
String数据库中所有关联证据主要来源于:实验数据、文本挖掘数据、数据库数据、基因邻接、基因融合、基因共表达。用户可以单独使用每种方法的数据,也可以组合使用。该系统会对不同方法得到的数据给予一定的权重,给出一个综合评分,以0-1的范围表示该互作关系的置信度。从11.0版本开始,String支持上传整个基因组水平的数据集,可以让用户把数据集可视化为互作网络,以及对整个输入的数据做基因富集分析,包括GO、KEGG富集分析。
如何使用String数据库
String数据库不需要注册,直接打开网站就可以使用。可以直接输入蛋白质名称或者蛋白序列进行查询。下面我们来看下String数据库具体如何操作吧!
1 、查询目标蛋白的互作信息
首先打开STRING数据库(https://string-db.org),点击主页的“Search”。选择“Protein by name”,输入目标蛋白或者基因名称,并在“Organism”中指定物种,然后点击“SEARCH”进入下一步。


2 、查询多个已知蛋白间的互作信息
选择“Multiple proteins”,输入蛋白名称,或者将所有蛋白名称整理到一个文件,直接上传文件即可。然后选择物种,点击search进入下一步。
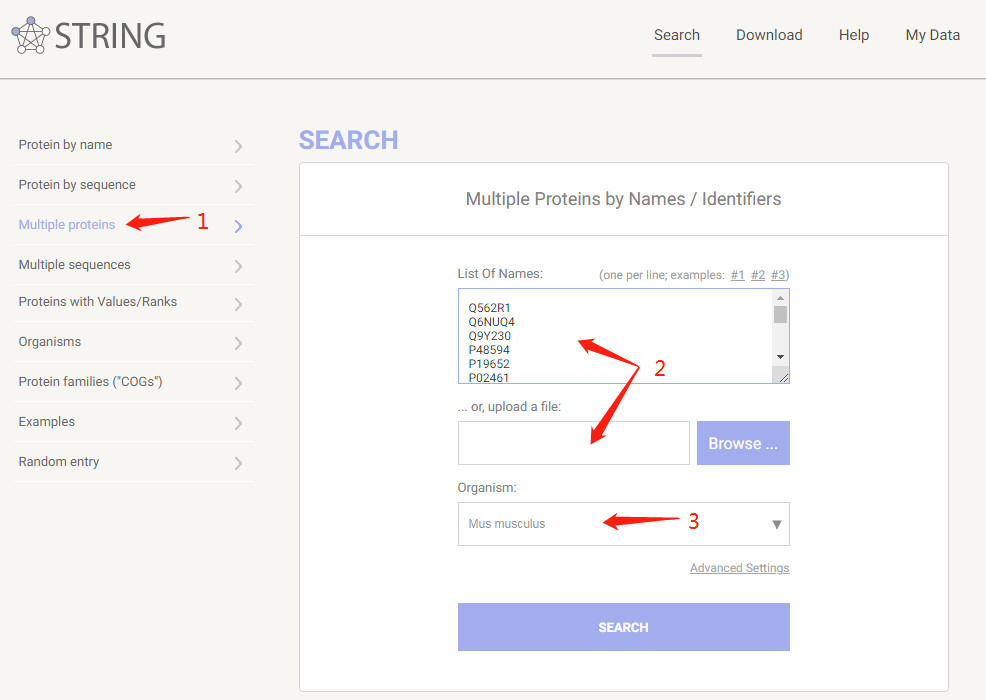
点击CONTINUE,得到最终的检索结果。
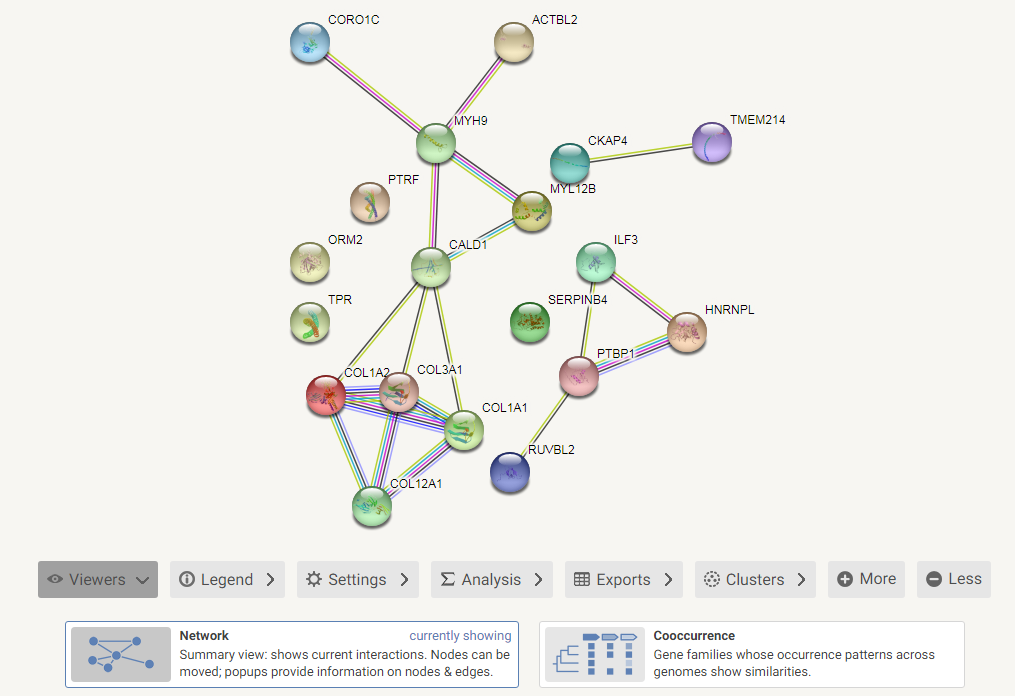
上图中的圆圈代表每个蛋白,有些圆圈内部有螺旋状的三维结构,代表该蛋白的结构已知,如果是未知结构的蛋白,圆圈内部为空。节点之间的连线表示蛋白之间的相互作用,不同颜色对应不同的相互作用类型,既包括实验验证的,也包括数据预测的,具体作用类型可以点击Legend查看。
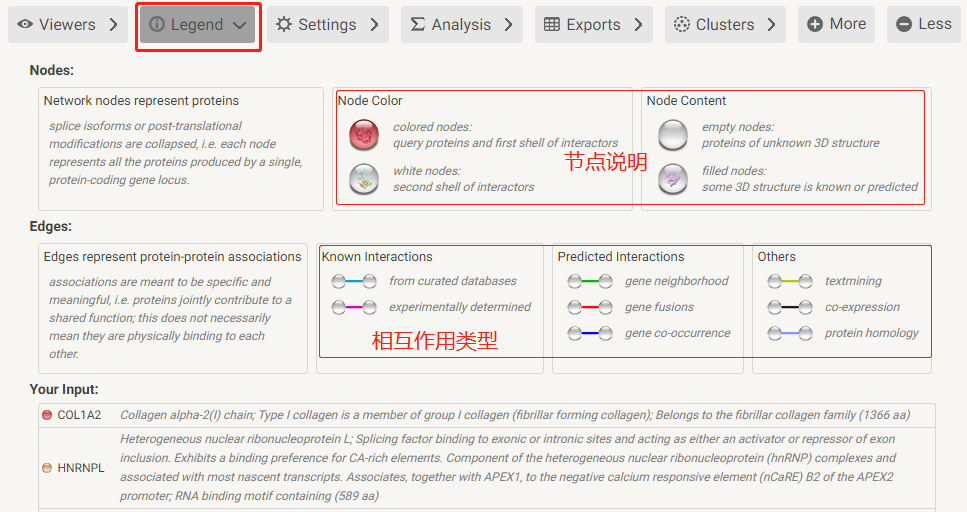
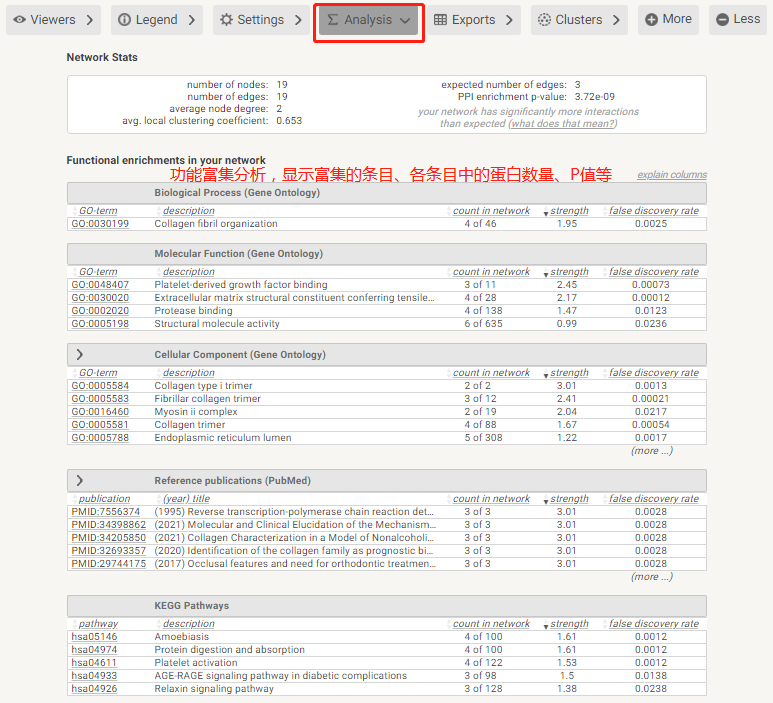
此外,String数据库还提供了互作网络蛋白的功能富集分析结果,包括GO、KEGG、Reactome等。
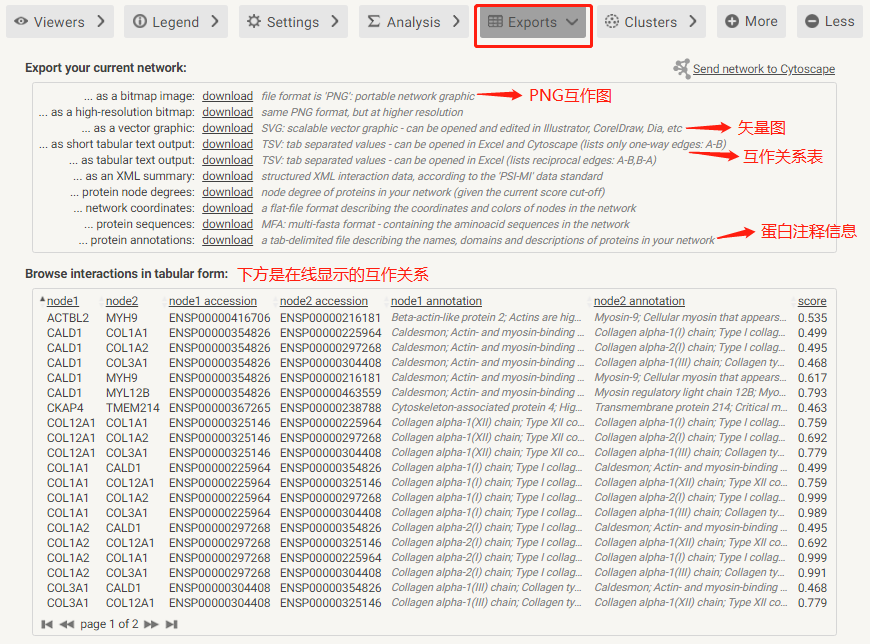
最后可以对互作网络结果进行导出,点击“Exports”,选择需要下载的数据即可。
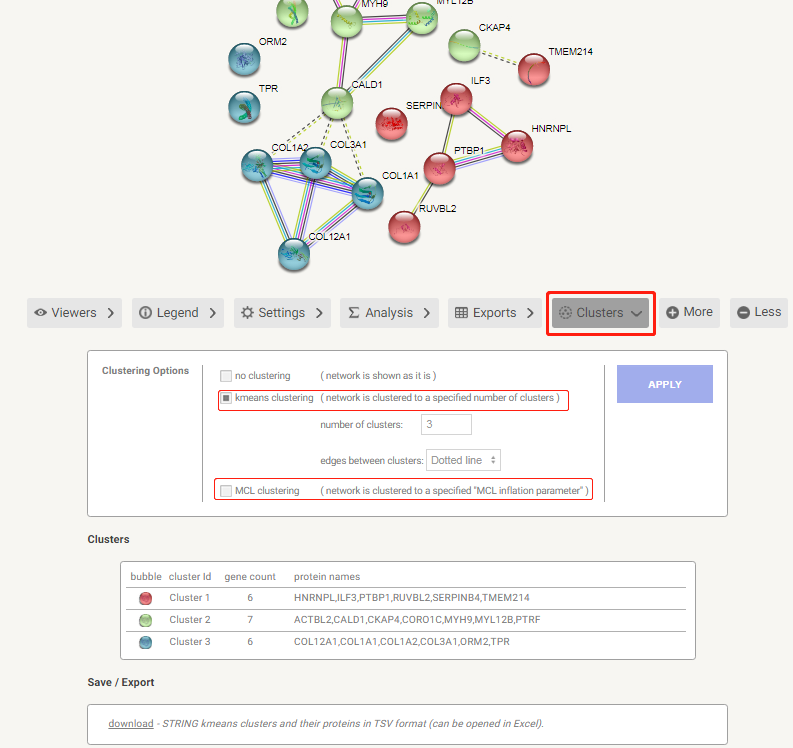
对于一个包含许多节点的蛋白质互作网络,还可以通过Clusters页面来挖掘其中的子网络信息,本质上是对基因进行聚类,从中可以看出哪些基因属于同一类。String支持kmeans和MCL聚类,聚类的结果为TSV格式网络图。
值得注意的是,点击“More”,可以加入更多的蛋白网络信息,连续点击可以持续加入更多蛋白。点击“Less”,即可删除前面增加的蛋白。以上就是对String数据库的全部介绍,具体信息请参阅官网说明。